2002 - 2004 中国科学技术大学,博士
2005 - 2006 金沙集团1862cc,助理研究员
2006 - 2011 美国斯隆-凯瑟琳癌症研究中心,博士后、副研究员、高级研究员
2011 - 至今 金沙集团1862cc,研究员
2015 - 至今 金沙集团1862cc大学,教授
2018年 北京市科学技术奖二等奖
2018年 政府特殊津贴
2017年 “长江学者奖励计划”特聘教授
2017年 HHMI国际青年学者
2017年 获得国家杰出青年基金
2017年 金沙集团1862cc优秀导师奖
2016年 第十三届中国青年女科学家奖
2016年 创新人才推进计划中青年科技创新领军人才
2016年 第九届谈家桢生命科学奖(创新奖)
2015年 细胞出版社2015中国年度论文奖
2015年 金沙集团1862cc优秀导师奖
2020年 博士程志获得地奥奖学金一等奖
2020年 博士程志获得研究生国家奖学金
2019年 博士尤李兰获得研究生国家奖学金
2019年 博士尤李兰获得金沙集团1862cc院长特别奖
2018年 博士李雪岩获得金沙集团1862cc院长优秀奖
2017年 硕士李雪岩、博士尹茂鲁获得研究生国家奖学金
2017年 博士李佳智获选参加第68届诺贝尔奖获得者大会
2017年 博士李佳智获选参加第十三届国际学生论坛
2016年 博士李佳智获得金沙集团1862cc院长优秀奖
2016年 博士李佳智获得研究生国家奖学金
2016年 博士赵宏图获得金沙集团1862cc大学优秀毕业生奖
2016年 硕士陈鹏获得金沙集团1862cc大学大学生奖学金
2015年 博士赵宏图获得金沙集团1862cc院长特别奖
2015年 博士赵宏图获得研究生国家奖学金
2015年 博士李佳智获得所长论文奖
2014年 博士赵宏图获得所长论文奖
研究工作主要集中在以下四个方面:
(1)第一大类CRISPR-Cas系统的作用机理研究
CRISPR-Cas广泛存在于原核生物中的一种由crRNA介导干扰系统,每一类包含不同的类型,第一大类分为I型、III型、IV型。本课题组通过生物化学与分子生物学、结构生物学等方法,成功解析了E.coli Cascade复合物结构,揭示了Cascade复合物的精确的组装方式(Zhao, Nature, 2014);发现了Cas1-Cas2识别外源入侵DNA分子机制,揭示了外源核酸片段的长度是如何确定的,该成果为揭示原核生物这一新的抵御病毒及遗传物质的入侵的机制奠定了重要的理论基础 (Wang, Cell, 2015);解析了不同状态的III-A型CRISPR-Cas系统效应复合物Csm的结构,并结合体内和体外的功能实验,系统地阐述了III型CRISPR-Cas系统抵御外源核酸的分子机制(You, Cell,2019)。
(2)第二大类CRISPR-Cas系统的作用机理研究
CRISPR-Cas系统的第二大类分为II型、V型、VI型。我们解析了结合有sgRNA的C2c1晶体结构,发现目的序列的碱基突变显著降低C2c1切割活性,该研究结果有助于开发新的基因组编辑工具,降低基因编辑过程中的脱靶现象(Liu, Molecular Cell, 2017)。解析了C2c2和C2c2-crRNA的晶体结构,揭示了C2c2剪切pre-crRNA以及切割靶标RNA的分子机制;同时也为改造CRISPR-C2c2系统在基因编辑领域的运用提供了强有力的理论依据 (Liu, Cell, 2017a);之后,本课题组进一步成功解析了Lbu细菌中Cas13a在多种状态下的结构,阐明了其分子机制,该成果为研究Cas13a发挥RNA酶活性的分子机制提供了重要的结构生物学基础(Liu, Cell, 2017b)。
解析了NmeCas9的五种不同状态的高分辨率结构,不仅揭示了两种不同的NmeCas9识别两种不同PAM的分子机制,还捕捉到了第一个Cas9活性状态下的结构,深入揭示了Cas9切割DNA的分子机制(Sun, Molecular Cell, 2019)。还解析了Cas12i2-crRNA和Cas12i2-crRNA-DNA复合物的晶体结构,揭示了Cas12i2对DNA的识别和切割机制,并首次观察到CRISPR-Cas系统效应蛋白的RuvC催化结构域活性状态的结构(Huang, Nature Communications, 2020)。
(3)Anti-CRISPR蛋白抑制CRISPR活性的机理研究
原核生物通过CRISPR-Cas系统抵抗噬菌体和质粒的入侵,而某些噬菌体也相应的进化出了自己的防御系统(Anti-CRISPR)。噬菌体编码的具有抑制CRISPR-Cas系统功能的蛋白被称为anti-CRISPR蛋白。我们多个anti-CRISPR 蛋白进行了研究,解析了AcrF3的高分辨率晶体结构与AcrF3-Cas3复合物的冷冻电镜结构(Wang,Cell Research,2016);并揭示了三个不同的Acr蛋白AcrIIC3、AcrIIC2、 AcrIIA2分别通过三种不同方式抑制Cas9 的分子机制(Sun, Molecular Cell, 2019; Thavalingam, Nature Communications, 2019; Liu, Molecular Cell, 2019)。
(4)小分子介导的基因沉默的结构生物学研究
我们发现某些原核生物的Ago蛋白不仅具有切割RNA的功能,还具有在小DNA分子介导下序列特异性的切割DNA的功能。通过解析系列的Ago蛋白与向导DNA以及靶DNA的三元复合物结构,我们揭示了Ago 蛋白切割DNA的分子机理 (Sheng, PNAS, 2014);发现单碱基凸起发生在引导链或者靶链对Ago结构和切割活性的影响不同, 揭示细菌Ago蛋白引导链与靶链不完全互补配对的分子机制(Sheng, Nucleic Acids Res., 2017);此外还在Agos蛋白指导导向DNA链切割靶标DNA链的机制研究上取得进展,在原子水平上阐明了细菌的Agos蛋白中参与切割活性的两个对称的精氨酸的重要意义(Lei, PNAS, 2019);并利用Ago蛋白设计出一种新型DNA荧光原位杂交方法,为染色质高阶结构研究以及基于FISH的临床分子诊断提供了方便而强大的工具(Chang, Nanoscale Horizons,2019)。
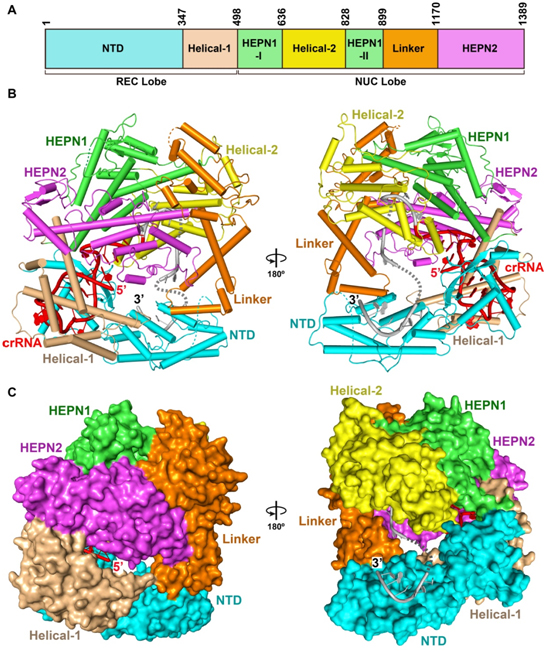
(来自Cell. 2017, 168:121-134)
1. Huang X, Sun W, Cheng Z, Chen M, Li X, Wang J, Sheng G*, Gong W* and Wang Y*. Structural basis for two metal-ion catalysis of DNA cleavage by Cas12i2. Nature Communications, 2020.10, online.
2. Sun W#, Yang J#, Cheng Z#, Amrani N, Liu C, Wang K, Ibraheim R, Edraki A, Huang X, Wang M, Wang J, Liu L, Sheng G, Yang Y, Lou J, Sontheimer E*, and Wang Y*. Structures of Neisseria meningitidis Cas9 Complexes in Catalytically Poised and Anti-CRISPR-Inhibited States. Molecular Cell, 2019, 76(6): 938-952.
3. You L, Ma J, Wang J, Artamonova D, Wang M, Liu L, Xiang H, Severinov K, Zhang X*, Wang Y*. Structure Studies of the CRISPR-Csm Complex Reveal Mechanism of Co-transcriptional Interference. Cell, 2019, 176, 239–253.
4. Liu L, Yin M, Wang M, Wang Y*. Phage AcrIIA2 DNA Mimicry: Structural Basis of the CRISPR and Anti-CRISPR Arms Race. Molecular Cell, 2019, 73, 611–620.
5. Lei J, Sheng G, Peter Pak-Hang Cheung, Wang S, Li Y, Gao X, Zhang Y*, Wang Y*, Huang X*. Two symmetric arginine residues play distinct roles in Thermus thermophilus Argonaute DNA guide strand-mediated DNA target cleavage, PNAS, 2019,116: 845–853.
6. Chang L#, Sheng G#, Zhang Y#, Shao S, Wang Y* and Sun Y*. AgoFISH: cost-effective in situ labelling of genomic loci based on DNA-guided dTtAgo protein. Nanoscale Horizons, 2019, 4:918-923.
7. Thavalingam A, Cheng Z, Garcia B, Huang X, Shah M, Sun W, Wang M, Harrington L, Hwang Sungwon Y, Reyes H, Sontheimer E, Doudna J, Davidson A, Moraes T*, Wang Y*, Maxwell K*. Inhibition of CRISPR-Cas9 ribonucleoprotein complex assembly by anti-CRISPR AcrIIC2. Nature Commun., 2019, 26;10(1):2806.
8. Yin M, Wang J, Wang M, Li X, Zhang M, Wu Q, Wang, Y. Molecular mechanism of directional CTCF recognition of a diverse range of genomic sites. Cell Research, 2017, 27(11):1365-1377.
9. Liu L, Li X, Ma J, Li Z, You L, Wang J, Wang M, Zhang X, Wang, Y. The Molecular Architecture for RNA-Guided RNA Cleavage by Cas13a. Cell, 2017. 170(4):714-726.
10. Sheng G, Gogakos T, Wang J, Zhao, H, Serganov A, Juranek S, Tuschl T, Patel D, Wang, Y. Structure/cleavage-based insights into helical perturbations at bulge sites within T. thermophilus Argonaute silencing complexes. Nucleic Acids Res. 2017, 45(15):9149-9163.
11. Liu L, Li X, Wang J, Yin M, Chen P, Wang M, Li J, Sheng G, Wang Y. Two Distant Catalytic Sites Are Responsible for C2c2 RNase Activities. Cell. 2017,168:121-134.
12. Liu L, Chen P, Wang M, Li X, Wang J, Yin M, Wang Y. C2c1-sgRNA Complex Structure Reveals RNA-guided DNA Cleavage Mechanism. Molecular Cell. 2017, 65.
13. Swarts D, Szczepaniak M, Sheng G, Chandradoss S, Zhu Y, Timmers E, Zhang Y, ZhaoH, Lou J, Wang Y, Joo C and Oost J. Autonomous Generation and Loading of DNA Guides by Bacterial Argonaute,Molecular Cell, 2017, 65(6):985-998.
14. Wang J, Ma J, Cheng Z, Meng X, You L, Wang M, Zhang X, Wang, Y. A CRISPR evolutionary arms race: structural insights into viral anti-CRISPR/Cas responses. Cell Research. 2016, 26:1165–1168.
15. Wang, J., Li, J., Zhao, H., Sheng, G., Wang, M., Yin, M. & Wang, Y., Structural and Mechanistic Basis of PAM-Dependent Spacer Acquisition in CRISPR-Cas System. Cell. 2015, 163: 840-853.
16. Zhao, H., Sheng, G., Wang, J., Wang, M., Bunkoczi, G., Gong, W., Wei, Z. & Wang, Y. “Crystal structure of the RNA-guided immune surveillance Cascade complex in Escherichia coli”, Nature. 2014, 151: 147-150.
17. Swarts, D. C., Makarova, K., Wang, Y., Nakanishi, K., Ketting, R., Koonin, E., Patel, D. J. & Oost, van der, J., “The evolutionary journey of Argonaute proteins”, Nature structural & molecular biology, 2014, 21: 743-753.
18. Swarts, D. C., Jore, M. M., Westra, E. R., Zhu, Y., Janssen, J. H., Snijders, A. P., Wang, Y., Patel, D. J., Berenguer, J., Brouns, S. J.J. & Oost, van der, J. "DNA-guided DNA interference by a prokaryotic Argonaute", Nature, 2014, 507: 258-261.
19. Sheng, G., Zhao, H., Wang, J., Rao, Y., Tian, W., Swarts, D. C., van der Oost, J., Patel, D. J. and Wang, Y. "Structure-based cleavage mechanism of Thermus thermophilus Argonaute DNA guide strand-mediated DNA target cleavage." Proc Natl Acad Sci U S A.2014, 111(2): 652-657.
20. Rüdel S, Wang, Y, Lenobel R, K?rner R, Hsiao HH, Urlaub H, Patel D, Meister G. Phosphorylation of human Argonaute proteins affects small RNA binding. Nucleic Acids Res. 2011,39:2330-43.
21. Wang, Y., Ludwig J., Schuberth C., Goldeck M., Schlee M., Li H., Juranek S., Sheng G., Micura R., Tuschl T., Hartmann G., Patel D., Structural and functional insights into 5'-ppp RNA pattern recognition by the innate immune receptor RIG-I. Nat Struct Mol Biol. 2010, 17:781-7.. 2010, 17:781-7.
22. Wang, Y, Juranek S, Li H, Sheng G, Tuschl T, Patel DJ. Nucleation, propagation and cleavage of target RNAs in Ago silencing complexes. Nature. 2009, 461:754-761.
23. Wang, Y, Juranek S, Li H, Sheng G, Tuschl T, Patel DJ. Structure of an argonaute silencing complex with a seed-containing guide DNA and target RNA duplex. Nature. 2008, 56:921-926.
24. Wang, Y, Sheng G, Juranek S, Tuschl T, Patel DJ., Structure of the guide-strand-containing argonaute silencing complex. Nature. 2008, 456:209-213.
25. Wang, Y, Liu L, Wei Z, Cheng Z, Lin Y, Gong W. Seeing the process of histidine phosphorylation in human bisphosphoglycerate mutase. J Biol Chem. 2006, 281:39642-8.
26. Wang, Y, Wei Z, Liu L, Cheng Z, Lin Y, Ji F, Gong W. Crystal structure of human B type phosphoglycerate mutase bound with citrate. Biochem. Biophys. Res. Commun. 2005, 331:1207-15.
27. Wang, Y, Wei Z, Bian Q, Cheng Z, Wan M, Liu L, Gong W,Crystal structure of human bisphosphoglycerate mutase, J. Biol. Chem. 2004, 279: 39132-8.
(资料来源:王艳丽研究员,2020-11-16)
王艳丽 博士 研究员 博士生导师
研究方向:(1)CRISPR/Cas系统的作用机理研究;(2)小分子介导的基因沉默的结构生物学研究
电子邮件:ylwang@ibp.ac.cn
电 话:010-64881316
通讯地址:北京市朝阳区大屯路15号(100101)
英文版个人网页:http://english.ibp.cas.cn/sourcedb/rck/EN_xsszmW/202005/t20200519_341374.html
课题组网站:/wylLab/